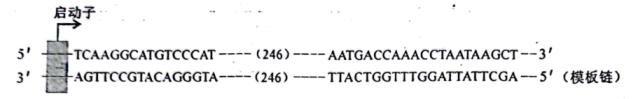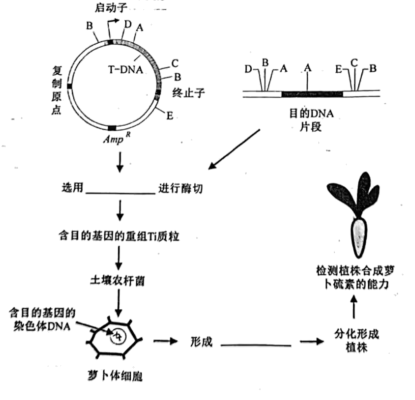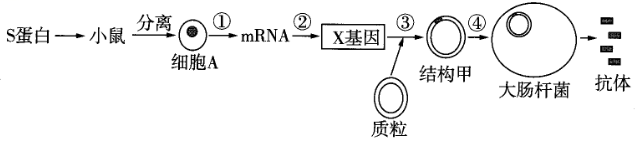
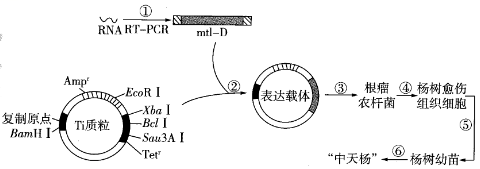
注:Ti质粒中的Tetr为四环素抗性基因,Ampr为氨节青霉素抗性基因。
限制酶 | BclⅠ | EcoRⅠ | XbaⅠ | Sau3AⅠ | BamHⅠ |
切割位点 | T↓GATCA | G↓AATTC | T↓CTAGA | ↓GATC | G↓GATCC |
①操作方法简便②目的性强,能定向改造生物性状③育种周期短④不受生殖隔离限制,能克服远缘杂交不亲和障碍⑤安全性高,对生态没有威胁

Mg2+浓度/(mmol·L-1) | 0 | 2 | 3 | 4 | 5 | 6 |
Ipp20基因相对含量 | - | + | ++ | +++++ | ++++ | +++ |
注:“-”表示未检测到Ipp20基因,“+”表示检测到Ipp20基因,且“+”越多,检测到的含量越多。
![]()
A.模板DNA被污染
B.引物特异性不强
C.加入原料过多

回答下列问题:

限制酶 | Ⅰ | Ⅱ | Ⅲ | Ⅳ |
识别序列及切割位点 | G↓GATCC CCTAG↑G | T↓GATCA ACTAG↑T | ↓GTAC CATG↑ | A↓AGCTT TTCGA↑A |


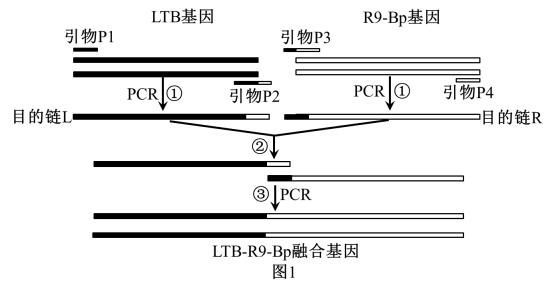
科研人员构建图1所示的表达载体,导入受体细胞。

启动子1为远红光诱导型启动子,启动子2 为持续表达启动子。据此分析,在没有远红光照射时, 受体细胞中 Cas9(N)、Cas9(C) 和 Cas9蛋白的存在状态及位置是。与持续表达 Cas9全酶相比,上述方法的优势是。
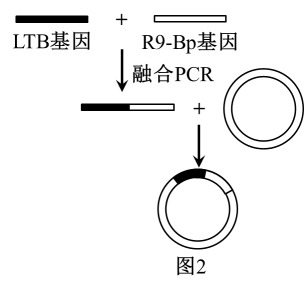
①检测本系统对目标基因PLK(一种肿瘤标志基因,可促进细胞分裂) 的编辑效果。实验过程如下:提取不同组别小鼠肿瘤细胞的DNA, PCR 扩增PLK 基因片段, 所得PCR产物热变性后降温复性。用T酶(可识别含错配碱基的 DNA并在错配处切割)酶切复性后的PCR产物,电泳检测结果如图2所示。

据图2 核酸电泳分离的 DNA分子大小可知此系统对目标基因进行了编辑,理由是。
②实验组小鼠的肿瘤明显小于对照组,分析原因是。
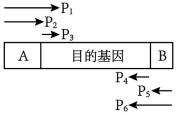
(i)导入目的基因的酵母菌应在的培养基上筛选培养。
(ii)由于需要导入多种酶基因,需要多次筛选,因此在导入一种目的基因后,要切除UGA基因,再重新导入。切去UGA基因的酵母菌应在的培养基上筛选培养。
实验目的 | 方法步骤要点 |
囊胚样品DNA提取 | 选取细胞提取DNA |
PCR引物的设计和合成 | 根据牛的SRY和CSN1S1基因序列设计合成引物 |
PCR扩增 | 预变性→变性→退火→延伸 |
鉴定分析 | |
对受体奶牛注射孕激素(或前列腺素) | |
胚胎移植 | 将符合要求的胚胎移植到受体奶牛的子宫内 |